2025
Type of resources
Available actions
Topics
INSPIRE themes
Provided by
Years
Formats
Representation types
Update frequencies
status
Resolution
GEMET keywords
-
Suites de traitements des données LiDAR à des formes d'ondes à 532 nm et 1064 nm acquises le 21 06 2024 à la Pointe d'Ailly. Dans l'attente d'une mise en ligne demander directement les données sources et résultats à patrick.launeau@univ-nantes.fr
-

Description détaillée : Des données de quantification bactérienne ont été obtenues pour 4 groupes bactériens (hétérotrophes, entérocoques, E.coli et Pseudomonas aeruginosa) avec la méthode cultivable et normalisée IDEXX, sur sédiments et eaux de ruissellement urbains collectés au site Django-R. La population microbienne multirésistante de plusieurs de ces groupes a également été quantifiée. - FORMAT Tableau excel avec onglets indiquant les données physicochimiques, les quantifications microbiologiques selon les matrices et les points de prélèvement des sédiments étudiés. - CONTEXTE : Les données présentées ont été produites par l’équipe UMR LEM–BPOE dans le cadre des projets de l’OTHU, dédiés à l’analyse de la qualité microbiologique des milieux impactés par les pratiques de gestion des eaux pluviales, en particulier les ruissellements urbains. L’objectif de ces travaux est d’évaluer la contamination microbiologique de ces milieux ainsi que la présence de bactéries tolérantes ou résistantes aux antibiotiques, à partir de matrices solides (sédiments) et liquides (eaux de ruissellement). Ces données sont la propriété de l'OTHU et de l'équipe BPOE de l'UMR Ecologie Microbienne, et sont sous embargo jusqu'à publication dans une revue scientifique ou pendant une période de 5 ans - LIEU : Métropole de Lyon et périphérie - PÉRIODE :entre novembre 2025 et janvier 2026
-

Photographie une fois par jour du bassin d'infiltration depuis le bungalow OTHU.
-

Photographie une fois par jour du bassin de rétention depuis le bungalow OTHU.
-
- DESCRIPTION DÉTAILLÉE : Données de séquençage du segment V4 de du gène de l’ARNr 16S pour les pelotes fécales de 5 mammifères (homme, chat, chien, mouton, campagnol) - FORMAT : Tableau Excel contenant le descriptif des échantillons, et les tables de contingence. - CONTEXTE : Ces données ont été produites dans le cadre des activités de l'OTHU et s'inscrivent dans les travaux multidisciplinaires de BPOE-LEM. Le but est la création d'une base de données de référence du gène 16S rRNA pour pouvoir par la suite identifier les sources de contamination fécale dans la métropole de Lyon. Cette base de données sera enrichie au fil du temps dès de nouveaux échantillons seront obtenus. Ces données sont la propriété de l'OTHU et de l'équipe BPOE de l'UMR Ecologie Microbienne, et sont sous embargo jusqu'à publication dans une revue scientifique ou pendant une période de 5 ans. - LIEU : Métropole de Lyon, Auvergne - PÉRIODE : 2025-maintenant
-
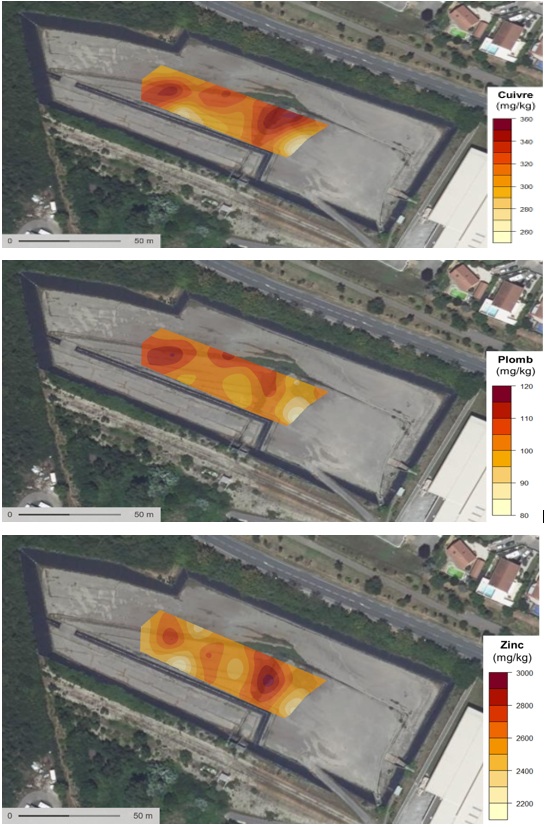
Les données ont été produites dans le cadre de l'OTHU à l'aide de la pXRF (spectrométire de flurorescence X portable) lors d'une campagne sur le site de Django Reinhardt à Chassieu le 13/10/2025. Les données rassemblent des mesures réalisées directement sur le terrain puis sur les mêmes échantillons en laboratoire avec séchage à l'étuve afin d'estimer l'impact de l'humidité sur les mesures.
 Catalogue de métadonnées
Catalogue de métadonnées